Zébrures blanches sur la peau : une nouvelle maladie génétique vient d'être identifiée à Dijon
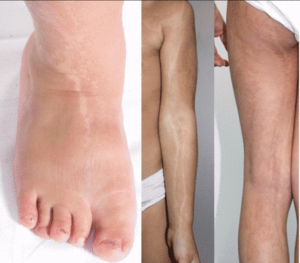
Certaines affections dermatologiques dessinent sur la peau des zébrures, des volutes, des tourbillons ou des éclaboussures en jet d’eau, une disposition qui a longtemps intrigué les dermatologues et qu’ils appellent « les lignes de Blaschko ». On sait maintenant qu’elles s’expliquent par des anomalies génétiques en mosaïque.
Les affections en mosaïque, qu’est-ce que c’est ?
Un organisme en mosaïque est constitué de populations distinctes de cellules qui diffèrent entre elles par leur patrimoine génétique, du fait de mutations apparues très tôt chez l’embryon. Ce phénomène de mosaïcisme peut se manifester sur la peau de diverses façons : par des bandes blanches ou pigmentées qui suivent les lignes de Blaschko, ou par différents types de « taches de naissance » : des angiomes, des nævus, qui se disposent plutôt en nappes arrondies ou rectangulaires. Un mosaïcisme peut aussi entraîner des anomalies de croissance limitées à une partie du corps ou d’un membre ou des malformations d’autres organes, tels que le cerveau.
Les nouvelles techniques de séquençage.
Les causes génétiques de ces affections en mosaïque étaient pour la plupart restées inconnues jusqu’à ces dernières années, du fait des limites de sensibilité des techniques d’analyse. Dès 2013, le laboratoire de recherche en génétique des anomalies du développement (GAD)*, dirigé par le Pr Laurence Faivre, a été l’un des premiers en France à développer la technique du séquençage à haut débit de l’exome, grâce à l’expertise du Dr Jean-Baptiste Rivière, aujourd’hui à Montréal, pour résoudre l’énigme des maladies rares sans diagnostic, permettant d’importantes avancées dans ce domaine. Le séquençage à haut débit permet, de plus, de détecter de faibles taux de mutations dans un tissu, ce qui est particulièrement utile dans les affections en mosaïque.
Une nouvelle maladie et un nouveau gène.
L’équipe du Pr Pierre Vabres, responsable du site de Dijon du centre national de référence MAGEC (Maladies rares de la peau et des muqueuses d’origine génétique, filière FIMARAD), a ainsi identifié chez six patients un même syndrome très rare puisque jamais encore rapporté, associant une dépigmentation et une dépilation en bandes disposées le long des lignes de Blaschko, des anomalies de croissance du visage et des extrémités, et une atteinte dentaire et oculaire. Chez tous ces patients, étudiés dans le cadre du travail de thèse du Dr Arthur Sorlin, ils ont trouvé dans la peau, par séquençage à haut débit de l’exome, des mutations identiques d’un même gène, RHOA. Jamais encore ce gène de la famille des RHO-GTPases, molécules essentielles au fonctionnement des cellules, n’avait été impliqué dans une affection congénitale.
« Ces mutations de RHOA ne touchent qu’une partie des cellules de l’organisme, et on pense qu’elles ne peuvent pas exister dans l’ensemble des cellules, sinon cela empêcherait le développement de l’embryon », explique le Pr Vabres. Ainsi, les cellules porteuses de la mutation ne peuvent survivre dans l’organisme qu’à l’état de mosaïque, où elles sont minoritaires. C’est l’hypothèse émise à la fin des années 1970 par le Pr Rudolf Happle, dermatologue à Fribourg (Allemagne), et qui a depuis lors été confirmée, comme dans le syndrome Protée ou le syndrome CLOVES, autres maladies rares en mosaïque dont le centre de référence MAGEC-Mosaïques de Dijon est également expert.
Un travail de coopération national et international
Les prélèvements des six premiers patients ont été recueillis dans le cadre du projet M.U.S.T.A.R.D. (Mosaic Undiagnosed Skin Traits And Related Disorders), coordonné à Dijon, grâce à une collaboration entre différents centres de génétique médicale et de dermatologie en France. Une septième patiente a été identifiée à Londres par l’équipe du Pr Veronica Kinsler. L’équipe du Pr Elizabeth Ross, à New York, a élucidé les conséquences des mutations de RHOA : la protéine ne pouvant plus assurer sa fonction, elle entraîne une forme anormale des cellules, ce qui pourrait expliquer les symptômes de la maladie. Il est cependant trop tôt pour savoir si cette découverte permettra des avancées thérapeutiques.
Une recherche menée dans le cadre d'un PHRC
Ces travaux ont pu être menés grâce à un soutien à la recherche par le Programme hospitalier de recherche clinique (PHRC), par des fonds publics de la Région Bourgogne (puis Bourgogne-Franche-Comté), du FEDER, de l’Université de Bourgogne et du CHU Dijon Bourgogne. L’équipe de recherche du Pr Vabres reçoit aussi des financements de la Société française de dermatologie et d’associations de patients atteints de maladies rares en mosaïque.
De nouvelles voies de recherche en génétique des maladies de la peau.
Le Pr Vabres et son équipe (@GAD_Mosaic sur Twitter) poursuivent leurs recherches sur les causes génétiques de nouvelles affections en mosaïque au sein du laboratoire GAD. Ils viennent de recevoir le soutien de l’Agence nationale de la recherche, qui a financé un projet collaboratif avec l’équipe du Dr Smahi, chercheuse Inserm à l’institut Imagine (Paris), portant sur le rôle des RHO-GTPases dans les maladies génétiques de la peau.
* l’équipe du centre de référence Maladies rares de la peau et des muqueuses d’origine génétique (MAGEC) du CHU Dijon Bourgogne intervient au sein du laboratoire Génétique des anomalies du développement (GAD), composant de l’UMR 1231 INSERM et de la FHU TRANSLAD - http://www.gad-bfc.org et www.translad.org
Commentaires 0 réactions
Soyez le premier à réagir !
Participez